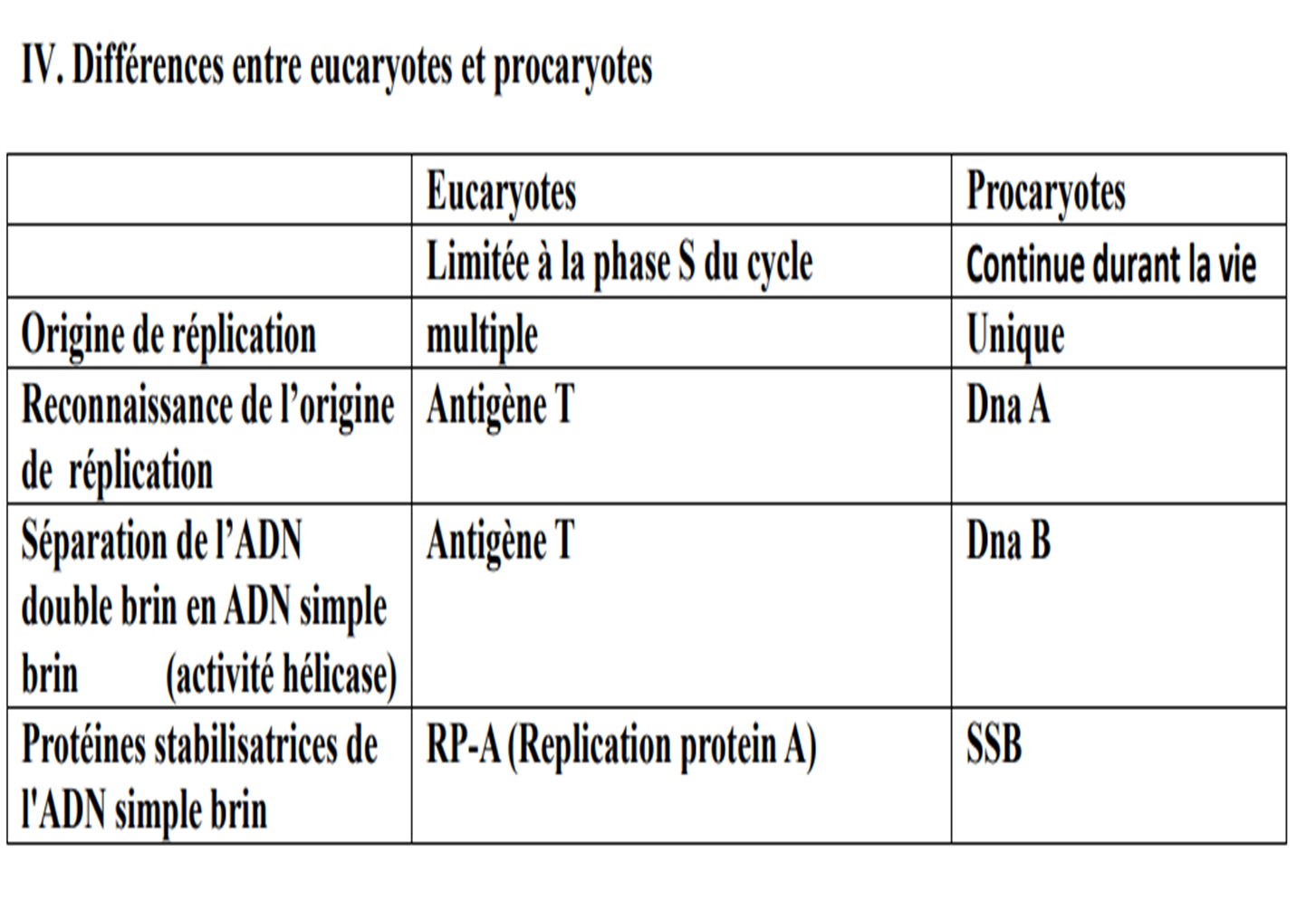
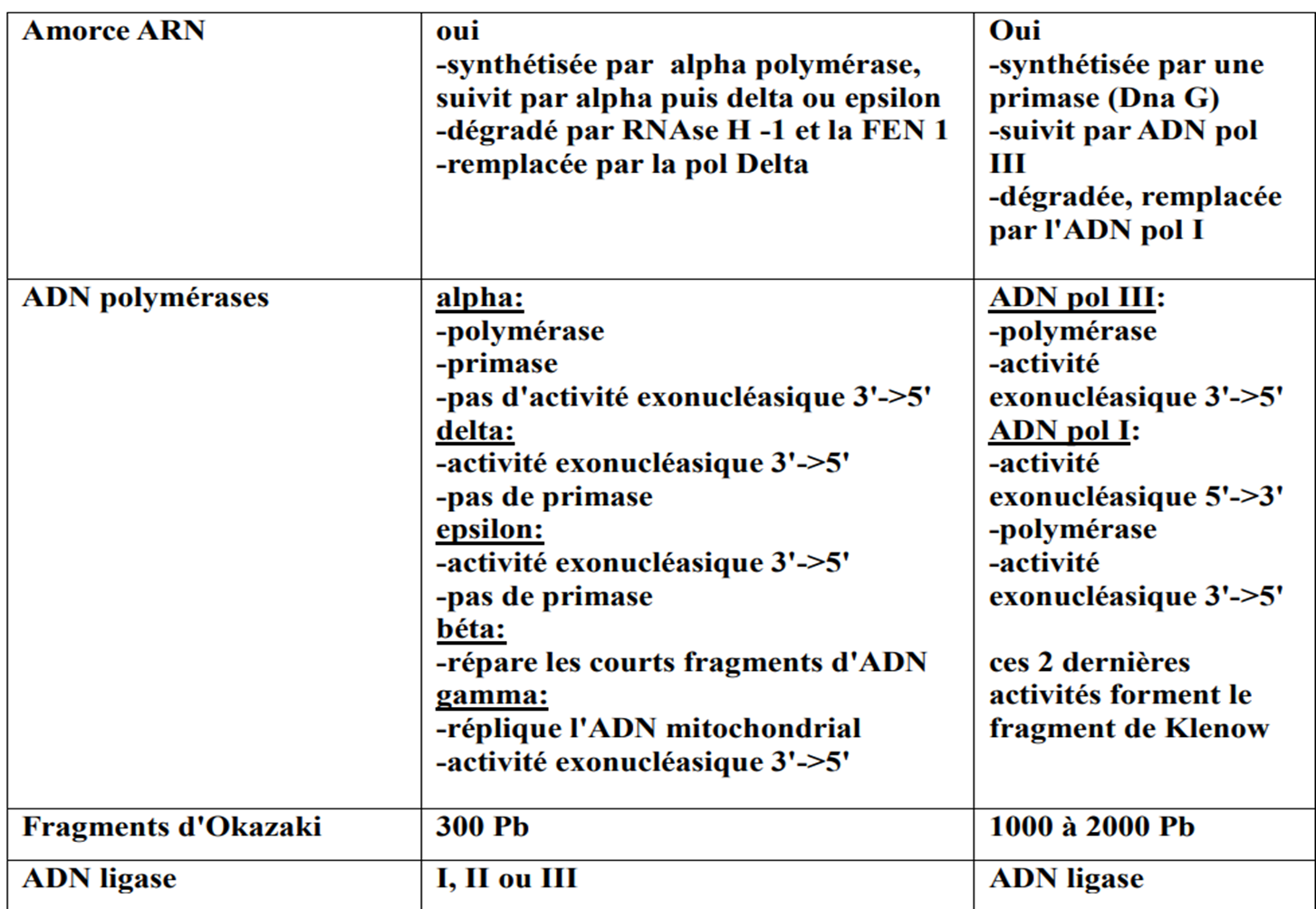
Rappel sur l'ADN:
Acide DésoxyriboNucléique ou ADN
u Molécule support de l'information génétique héréditaire : Les gènes sont des segments d'ADN.
u C'est un des constituants des chromosomes.
L'ADN se situe :
- Situées dans le noyau chez les eucaryotes.
- Situées directement dans le cytoplasme de la cellule chez les procaryotes.
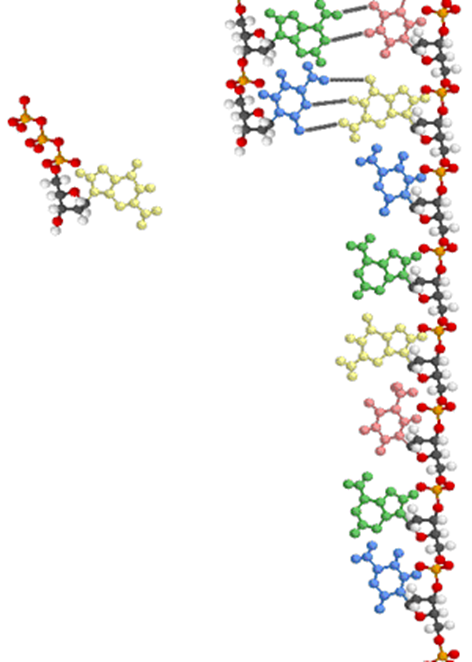
u Structure l'ADN : formée de deux brins complémentaires enroulés en hélice (double hélice).
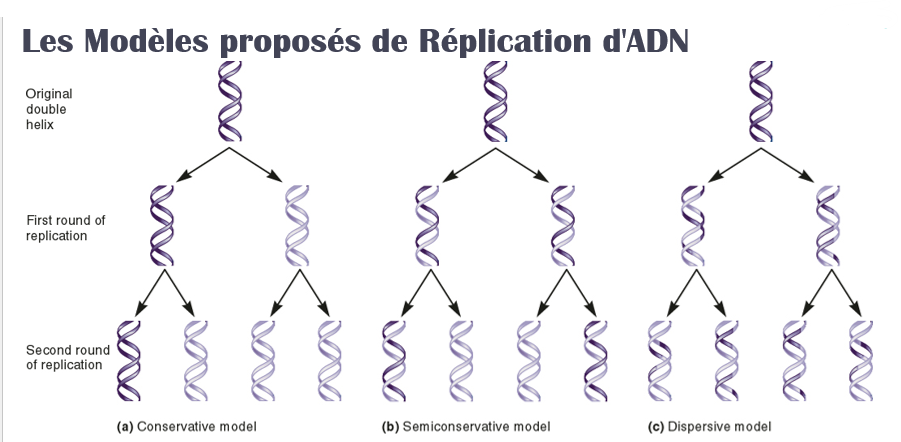
Les modèles proposés de la réplication de l'ADN:
Dans les années 1950, trois mécanismes différents ont été proposés pour la réplication d'ADN.
u Théorie conservatrice : Les deux brins parentaux restent intacte après la réplication d'ADN
u Théorie Semi conservatrice : Chacune des molécules d’ADN filles se compose d’un brin parente et d’un nouveau brin.
u Théorie Dispersive : Les molécules d’ADN parents et filles sont décomposées en fragments

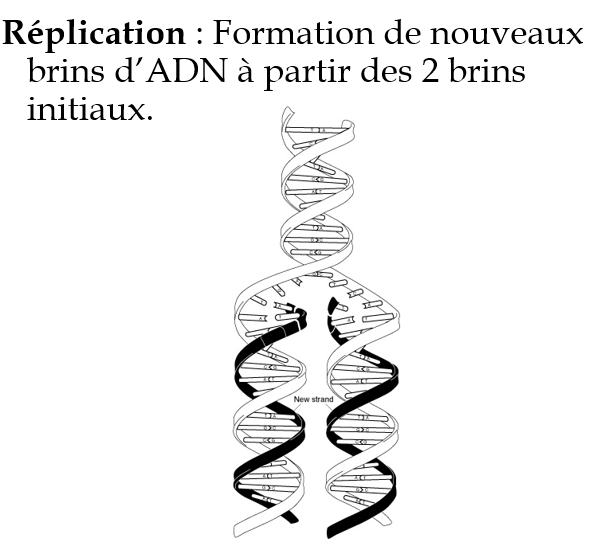
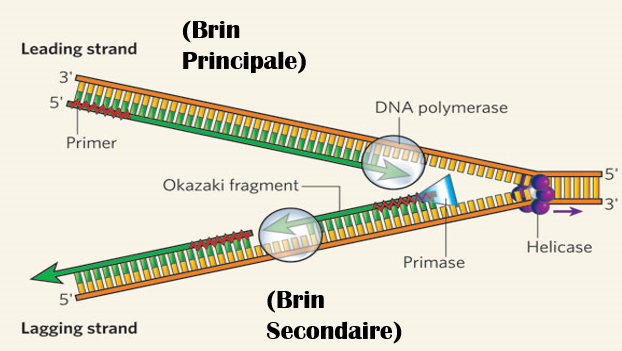
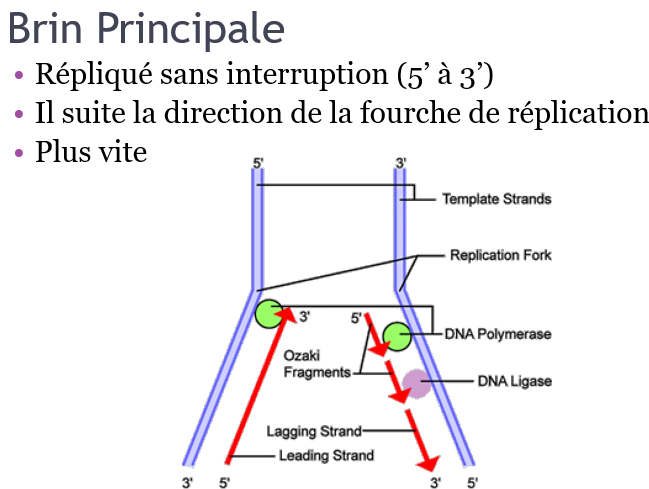
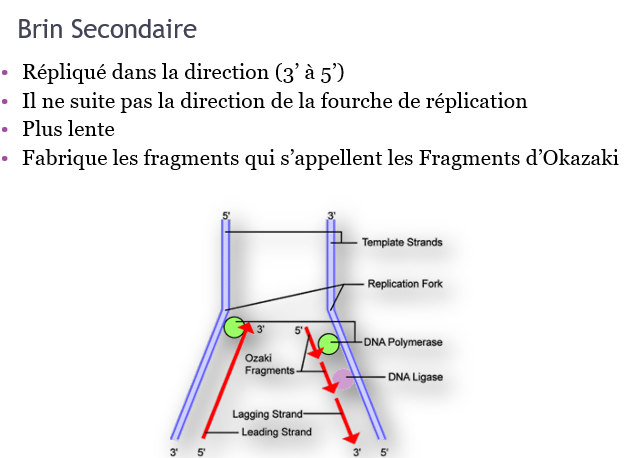
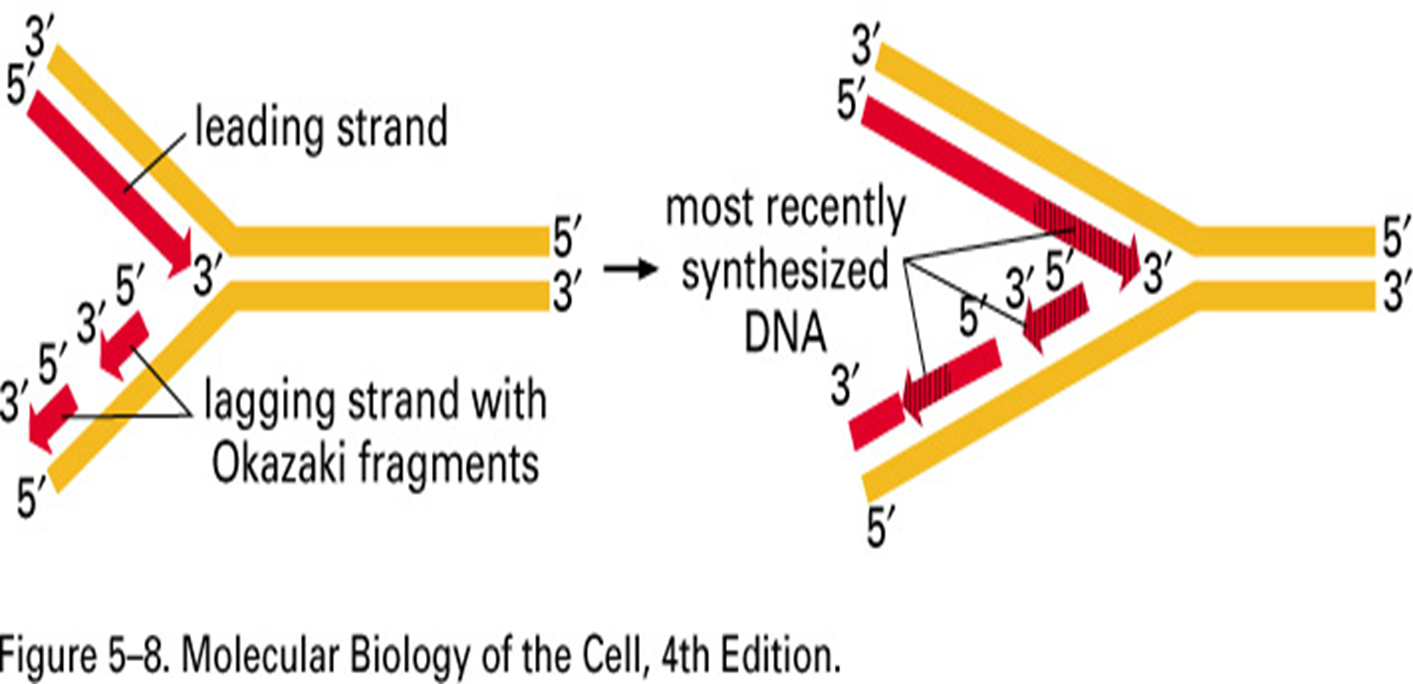
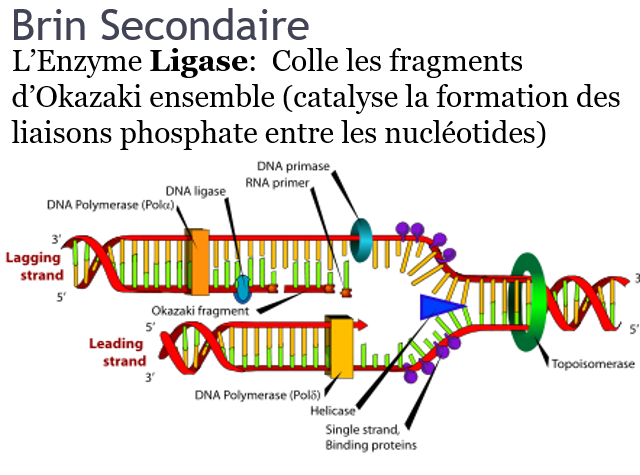
2. Élongation: deux nouveaux brins d’ADN sont assemblés en utilisant l’ADN parental comme matrice.
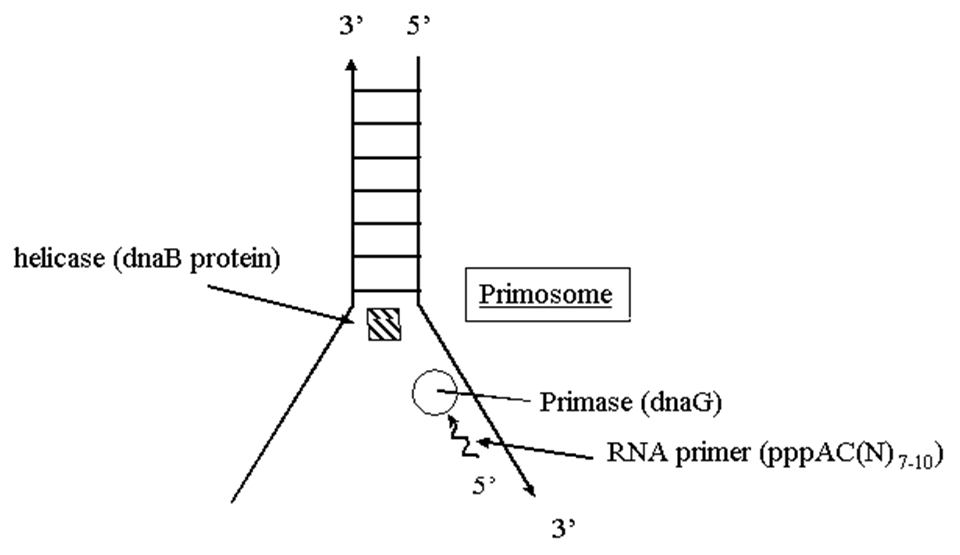
L’enzyme ARN Primase: Synthétise une pièce d’ARN pour commencer le processus d’élongation.
L’Enzyme ADN Polymérase: Commencent à ajouter un nucléotide à la fois pour créer un nouveau brin complémentaire.
• Initiation -La réplication débute au niveau des origines de réplication. L’antigène T reconnait ce site d’initiation, s’y fixe et entraine l’ouverture de la double hélice d’ADN par son activité hélicase ; la protéine RP-A se fixe aux régions d’ADN simple-brin pour prévenir leur réassociation.
L’ADN polymérase α (Pol α) synthétise l’amorce ARN-ADN de chaque brin continu et de chaque brin discontinu, grâce à son activité primase, suivi d’un fragment d’ADN de 20 à 30 nucléotides grâce à son activité ADN polymérase. B. Elongation -La protéine RF-C (replication factor C) reconnait le complexe matrice-amorce et recrute la protéine PCNA (Proliferative Cell Nuclear Antigen) qui provoque le remplacement de l’ADN polymérase α par l’ADN polymérase δ ou l’ADN polymérase Ɛ, cette dernière reprend la synthèse pendant que l’antigène T continu à fonctionner comme hélicase et que la topoisomérase I relâche la tension devant la fourche de réplication.